Sistema modular con Cariotipador y FISH para estudio de citogenética humana.
Consiste en los siguientes módulos independientes:
MetaClass Cariotipador MetaClass FISH MetaClass Base de datosMás información:
MetaClass Cariotipador
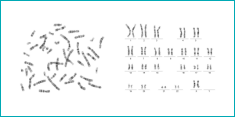
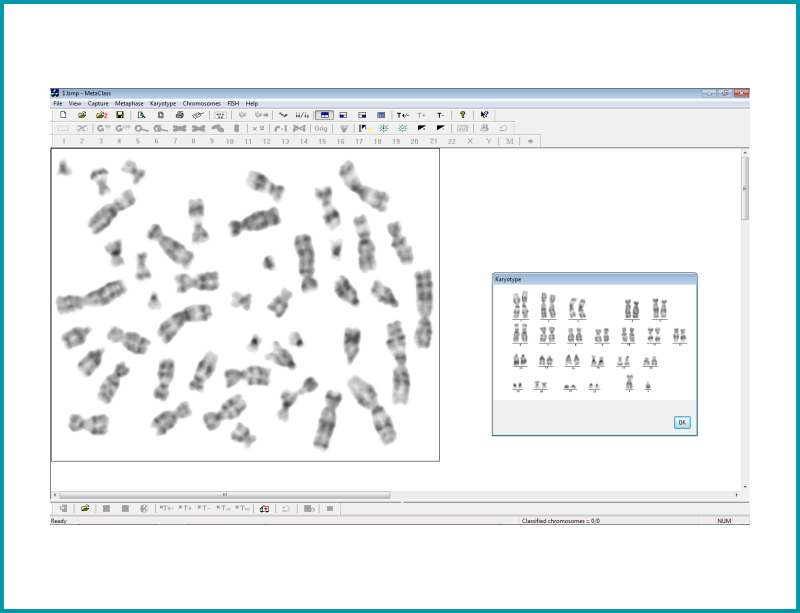
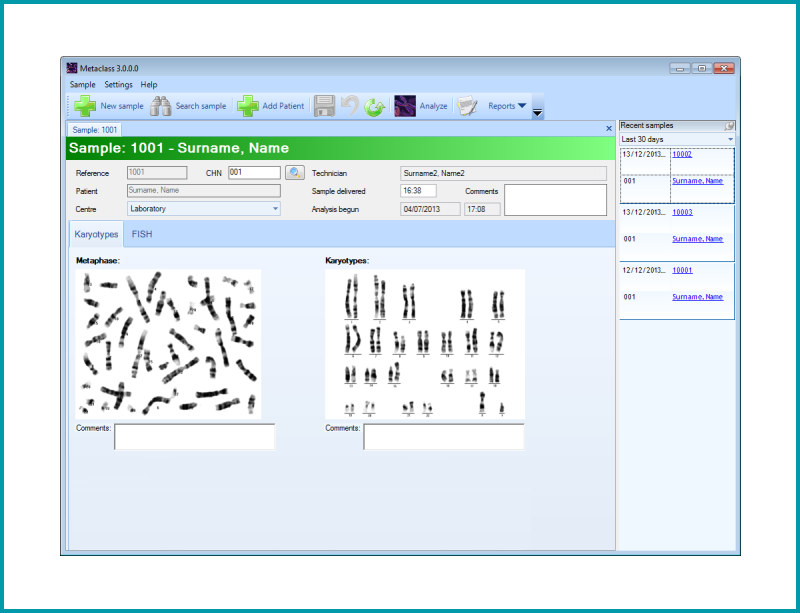
Permite obtener el cariotipo de una muestra a través de la captura de una serie de imágenes de la metafase. El citogenetista puede observar cualquier cambio en los cromosomas. Cada cromosoma se colocará por pares de acuerdo con su tamaño, la posición de los centrómeros y la disposición de las bandas visualizadas.
El sistema proporciona una excelente morfología y calidad de las bandas de cromosomas.
Como resultado final, se obtiene un informe personalizado.
| El cariotipo se analiza en microscopía de campo claro. Con el objetivo 100X |
| Se pueden capturar varias imágenes de la metafase |
| El umbral se puede modificar para mejorar la calidad de la imagen |
| Clasificación automática de los cromosomas |
| El modulo ofrece 3 vistas en la pantalla: La vista de la metafase, cariotipo y cromosomas no clasificados que se marcan con un 0 |
| Se puede mostrar el prototipo del cromosoma |
| Los cromosomas no clasificados se pueden corregir de forma automática o manualmente de: – Superposición: Cuando un cromosoma aparece superpuesto con otro, en una parte. – Separación: Cuando dos cromosomas están juntos en un extreme, se pueden separar. – Cruces – Enderezar – Rotación – Voltear un cromosoma – Obtener la imagen especular, así como la magnificación de los cromosomas individuales. – El brillo y contraste se pueden modificar. – Las bandas dañadas de los cromosomas se pueden señalizar en el cariotipo |
| Se pueden guardar las sesiones *mtc y las imágenes * bpm. |
| Se pueden seleccionar cromosomas individuales y exportarlos al Gestor de muestras (Metaclass Base de datos) para añadir comentarios en los resultados e imprimir el informe. |
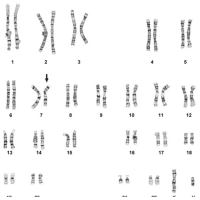
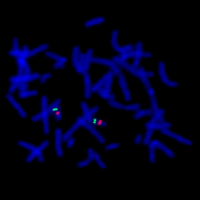
Cariotipo con Síndrome de Down (trisomía 21)
Esta es la anomalía cromosómica más común en neonatos. Se caracteriza por tener un cromosoma 21 extra, y se escribe de la siguiente manera: 47, XY,+21
A continuación la descripción del cariotipo:
47: El número total de cromosomas (46 es lo normal). XY: Los cromosomas sexuales (masculino). +21: Designa el cromosoma 21 extra.Cariotipo con Delección en el cromosoma 7
Este cariotipo es un ejemplo de una delección simple de un cromosoma. En este caso, un segmento en el brazo q, o largo, del cromosoma derecho 7 está ausente. En este ejemplo particular hay dos roturas microscópicas visibles que muestran la delección instersticial. Si hubiera existido una rotura como resultado de la pérdida de la parte final del cromosoma, ésta se conoce como delección terminal. El Cariotipo se escribe como: 46,XY, del(7) (q11.23q21.2).
A continuación la descripción del cariotipo:
46: El número total de cromosomas. XY: Los cromosomas sexuales (masculino). del(7): delección en el cromosoma 7. (q11.23q21.2): puntos de rotura del segmento ausente.MetaClass FISH
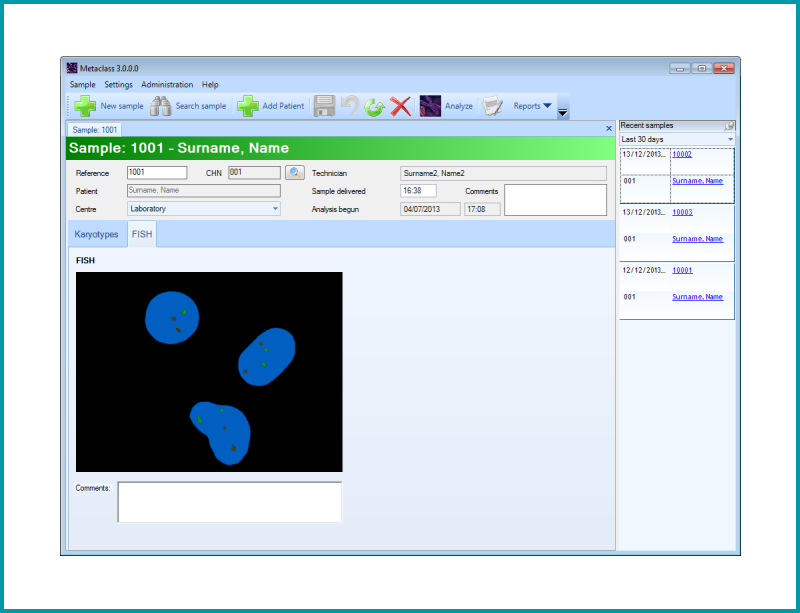
Módulo de análisis para obtener la imagen Fluorescent IN SITU Hybridization (FISH).
Las imágenes de fluorescencia capturadas de muestras hibridadas con varias sondas de ADN, permiten confirmar anomalías genéticas o cromosómicas, tales como trisomías, microdelecciones o algunas reordenaciones cromosómicas.
| Las imágenes de FISH se analizan con microscopía de fluorescencia, con el objetivo 100X oil |
| Se capturan varias imágenes con diferentes filtros. Las imágenes son originalmente en b/n para finalmente obtener una única imagen resultante que muestra la presencia o ausencia de la señal. |
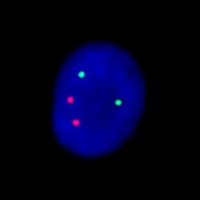
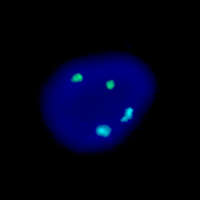
Este es un ejemplo del Screen test de Aneuplodía, donde núcleos de células del líquido amniótico en interfase se han combinado con varias sondas de ADN para los cromosomas 13,18,21, X e Y. El núcleo de la izquierda ha sido hibridado con sondas para el cromosoma 13 (green), y 21 (red). El núcleo de la derecha se ha hibridado con sondas para el cromosoma 18 (aqua), X (green), e Y (red). Hay dos señales para cada uno de los cromosomas 13,18 y 21 y una señal para el X y una para la Y. Por lo tanto, en lo referido al Screen test de Aneuploidía, este es un feto normal de sexo masculino.
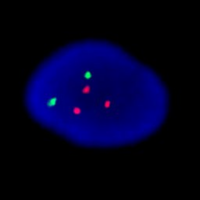
El test de Aneuploidía muestra un feto de sexo femenino con trisomía 21. El núcleo de la izquierda se ha hibridado con sondas para el cromosoma 13 (green), y 21 (red) y muestra claramente 3 señales. El núcleo de la derecha se ha hibridado con sondas para los cromosomas 18 (aqua), X (green) e Y (red). Como muestra dos señales verdes y ninguna roja se trata de un feto femenino.
Este es un ejemplo de metafase celular que ha sido hibridado con una sonda para el síndrome Shprintzen ShDiGeorge/Velo-Cardio-Facial/CATCH 22/, causada por una microdelección en el cromosoma 22. En este caso particular, la sonda es una mezcla de dos colores para el cromosoma 22. La señal verde es un control interno y se localiza en el 22q13. Permite la rápida identificación de los dos cromosomas 22. La señal roja se localiza en la región DiGeorge 22q11.2. En este caso en particular, los dos cromosomas 22 muestran la señal roja, no hay microdelección en el region DiGeorge y por lo tanto no presenta el síndrome DiGeorge.
MetaClass Base de datos
Base de datos integrada que se puede instalar con cualquiera de los módulos arriba descritos, permite almacenaje de los datos de los pacientes y acceso fácil a los resultados finales e informes.
El módulo incluye informes personalizados en cualquier idioma.