Le système modulaire Caryotypage et FISH est utilisé dans le cas des études cytogénétiques humaines.
Il se constitue des modules indépendants suivants :
Metaclass Caryotypage MetaClass FISH Metaclass Base de donnéesPour plus d’informations:
Metaclass Caryotypage
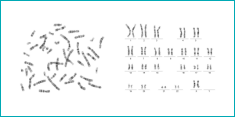
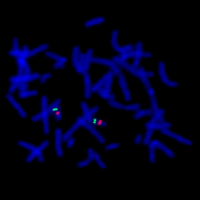
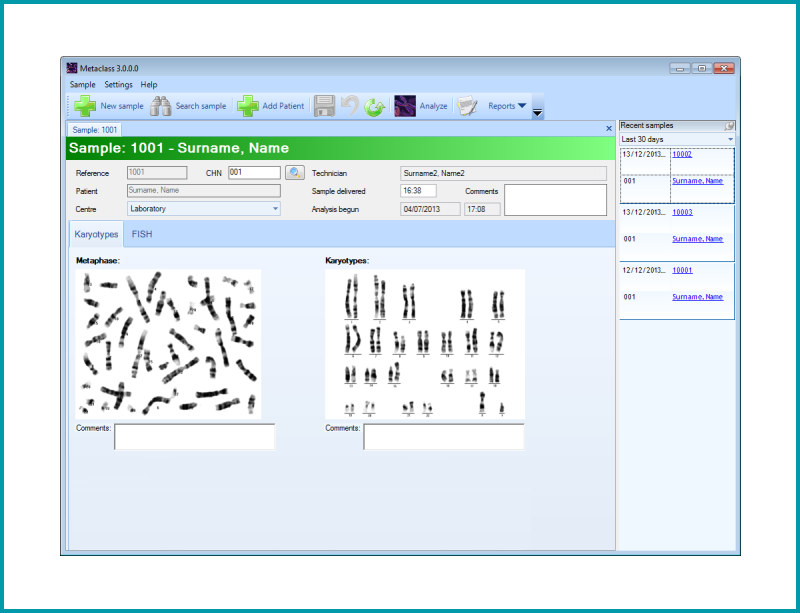
Il permet l’étude du caryotype à travers les captures d’images digitales obtenues à partir d’une métaphase. Le cytogénéticien peut examiner tout changement structural dans les chromosomes. Chaque chromosome peut être rangé par pairs selon la taille, on peut visualiser la position des centromères et la disposition des bandes.
Le système donne une excellente morphologie et qualité aux bandes chromosomiques.
Pour résultat final, le rapport, fournit par le système, est personnalisé.
| L’étude du Caryotype est analysée sous microscope en champ clair. Avec l’objectif 100x. |
| Plusieurs images de métaphases peuvent être capturées. |
| Le seuil peut être modifié afin d’améliorer la qualité de l’image capturée. |
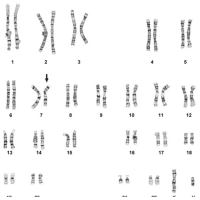
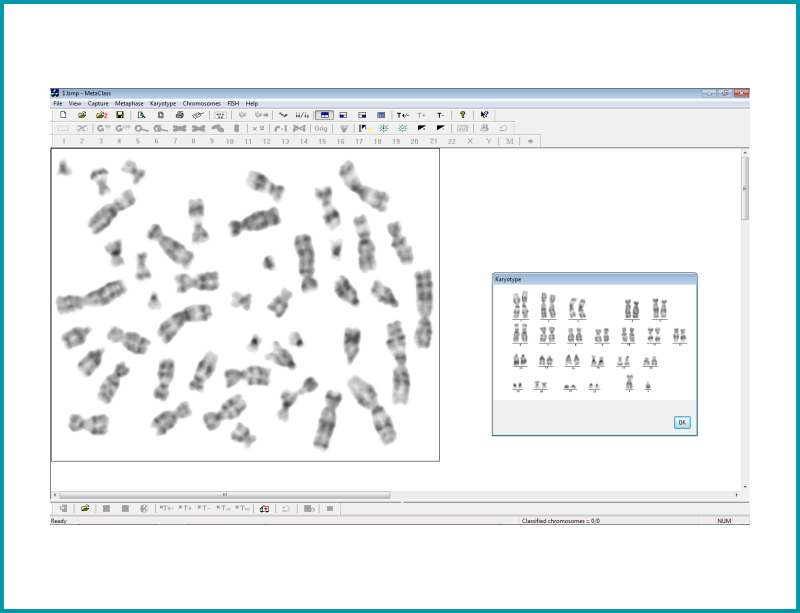
| Classification automatique des chromosomes |
| Le module offre 3 vues sur l’écran: vue Métaphase, le Caryotype et une des chromosomes non classés marqués par un 0. |
| Il est possible d’afficher le prototype du chromosome. |
| Les chromosomes non-classés peuvent être automatiquement corrigés, ou manuellement si désiré, pour les éléments suivants : – Superpositions : Un chromosome apparait superposé à un autre sur une partie. – Séparation : Quand deux chromosomes se joignent à un extrême, ils peuvent être automatiquement séparés. – Croisements – Redresser – Rotations – Retourner un chromosome – Obtenir l’image spéculaire, ainsi que un grossissement de chaque chromosome. – La brillance et le contraste peuvent être modifiés et automatiquement obtenus. – Les bandes de chromosomes endommagées peuvent être signalées dans l’étude du caryotype. |
| Fichiers de session *mtc ou les images *bpm peuvent être sauvegardés. |
| Les chromosomes individuels peuvent être sélectionnés et exportés vers le logiciel de gestion des échantillons (Base de données Metaclass) pour ajouter des commentaires aux résultats et imprimer le rapport final. |
Caryotype avec le Syndrome de Down (trisomie 21)
C’est l’anomalie la plus répandue chez les nouveau-nés. Elle est caractérisée par un chromosome supplémentaire 21 et le caryotype s’écrit de la manière suivante: 47, XY,+ 21.
La description du caryotype est la suivante:
47: le nombre total de chromosomes (46 c’est le normal). XY: les chromosomes sexuels (masculins). 21: désigne le chromosome supplémentaire comme un 21.Caryotype avec délétion du chromosome 7
Ce caryotype est un exemple d’une délétion pure et simple d’un chromosome. Dans ce cas, un segment au sein de la q, ou le bras long du chromosome droit 7, est absente. Dans cet exemple particulier, il existe deux ruptures visibles au microscope à l’intérieur du bras long qui montrent une délétion interstitielle. S’il y avait eu une rupture résultant de la perte de l’extrémité d’un chromosome, cela s’appellerait une délétion terminale. Le caryotype s’écrit: 46, XY, del (7) (q11.23q21.2).
La description du caryotype est la suivante:
46: le nombre total de chromosomes. XY: les chromosomes sexuels (masculins). del (7): délétion du chromosome 7. (q11.23q21.2): les points de déchirure du segment absent.Metaclass FISH
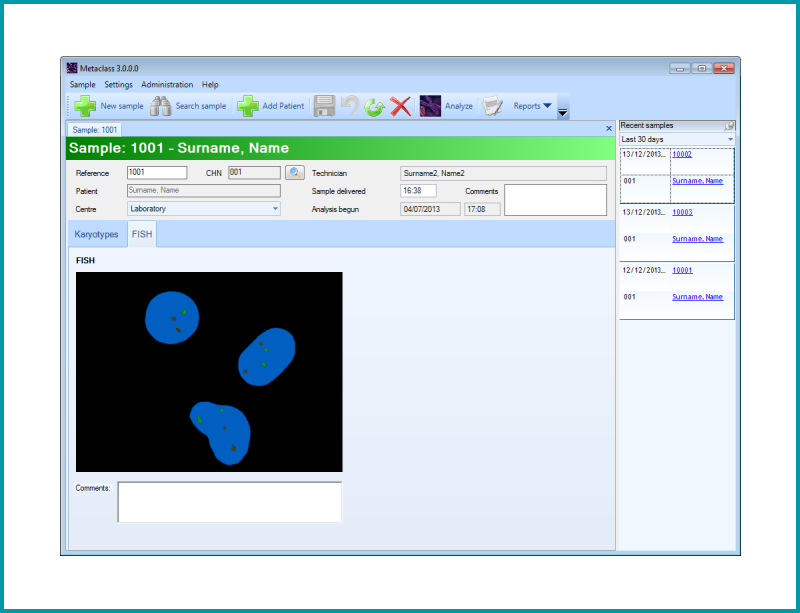
Module d’analyse pour obtenir l’image Fluorescent IN SITU Hybridization (FISH).
Les images capturées utilisant les sondes d’ADN marquées par fluorescence, permettent la confirmation des anomalies génétiques ou chromosomiques telles que les trisomies, micro délétion ou quelques remaniements chromosomiques.
| Les images FISH sont analysées sous microscope de fluorescence, avec l’objectif 100x (huile). |
| Plusieurs images peuvent être capturées avec différents filtres. Les images sont originellement en b/w, mais fournit une image finale de couleur unique qui montre la présence ou l’absence du signal. |
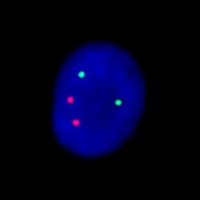
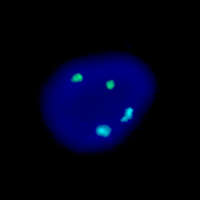
Ceci est un exemple du Aneuploid Screen test, où les noyaux de cellules de liquide amniotique en interphase ont été combinés avec plusieurs sondes d’ADN pour les chromosomes 13, 18, 21, X et Y. Le noyau représenté sur l’image de gauche a été hybridées par des sondes pour le chromosome 13 (vert), et 21 (rouge). Le noyau sur l’image de droite a été hybridé à des sondes pour les chromosomes 18 (Aqua), X (vert), et Y (rouge). Comme il ya deux signaux pour chaque chromosomes 13, 18, et 21 et un signal pour chaque chromosome, un pour X et un autre pour Y. D’après le Aneuploid Screen test, c’est un fœtus normal de sexe masculin.
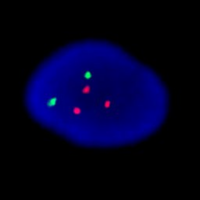
Ce test du Aneuploid Screen montre un fœtus de sexe féminin avec la trisomie-21. Le noyau de l’image de gauche a été hybridé par les sondes pour les chromosomes 13 (vert), et 21 (rouge) et montre clairement trois signaux. Le noyau de droite a été hybridé avec des sondes pour les chromosomes 18 (Aqua), X (vert), et Y (rouge). Comme il dispose de deux signaux verts et aucun signal rouge, il s’agit d’un fœtus féminin.
Ceci est l’exemple d’une cellule en métaphase qui a été hybridée avec la sonde pour le Syndrôme Shprintzen/DiGeorge/Velo-Cardio-Facial/CATCH 22/ qui est causée par une micro délétion du chromosome 22. Dans ce cas particulier, la sonde est un mélange bi-couleur de deux sondes distinctes pour le chromosome 22. Le signal vert est un contrôle interne et se localise dans le 22q13. Il permet d’identifier rapidement des chromosomes 22. Le signal rouge est situé dans la région de Di George à 22q11.2. Dans ce cas particulier, les deux chromosomes 22 ont le signal rouge dans cette cellule, il n’y pas de micro délétion dans la région de Di George et par conséquent cet individu n’a pas le syndrome de Di George.
MetaClass Database
C´est une base de données intégrée qui peut être installée avec n’importe quel module d’analyses décrits ci-dessus permettant non seulement le stockage des données des patients mais aussi un accès facile aux résultats finaux et aux rapports.
Le module comprend des rapports personnalisés disponible dans n’importe quelle langue.